数据处理
采用
Proteome Discoverer 软件 2.1 版本(PD 2.1)进行数据处理。该软件的特色是提供了全新改进版的 TMT
定量分析工作流程,其新功能包括:1)可用于添加报告离子同位素分布的全新用户界面;2)解析 TMT10plex
试剂中报告离子同位素杂质的能力;3)实现基于信噪比(S/N 值)的 TMT 定量分析;4)根据 S/N 值归总进行蛋白质和肽段定量分析;
5)提供对肽段和蛋白质丰度值进行归一化和标准化新方法。
在 Proteome Discoverer 2.1 软件中设置数据处理流程的关键步骤详细描述如下:
1. 建立研究专用定量分析方法
在开始新研究之前,通常需要先更新定量分析方法,其编辑流程为:
1. 进入 Administration,选择 Maintain Quantification Methods。其中提供了常用定量分析方法的模板。
2. 选择 Add,从已有方法中选择模板。每个已有 TMT 定量分析模板都包含了残基/肽段氮端的修饰和报告离子的同位素分布。
3.同位素分布值应按照该研究所用
TMT 试剂分析证书(CoA)中提供的信息进行添加。相关信息可在
http://www.thermofisher.com/order/catalog/product/90110?ICID=search-product
上通过试剂瓶上的批次号查询获得。
4. 根据研究需要,在“active”列中选择/去除报告离子通道。
5. 保存新创建的定量分析方法。新创建的研究专用定量分析方法参见图 1。
2. 导入 FASTA 数据库
1. 在 Administration 条目下打开 Maintain FASTA Files。
2. 用 Add 功能导入本地硬盘上已有的 .FASTA 文件。
3. 另一种方法是使用 Download 功能,键入 taxonomy ID,从蛋白质中心下载数据库文件。
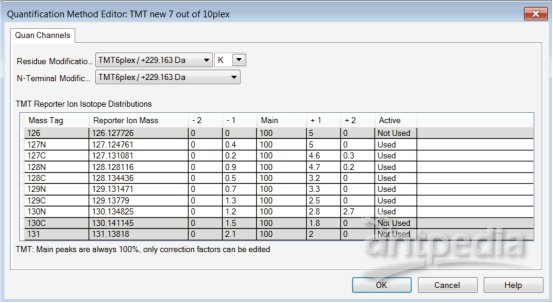
图 1. 用户定义的研究专用 TMT10plex 定量分析方法示例。
3. 创建新研究
1. 在 Proteome Discoverer 软件起始页面选择 New Study and Analysis(图 2)。
2. 定义 Study Name 并指定 Study Directory,将文件保存在特定的文件夹中。
3.
若要进行 Processing Workflow,通过倒三角图标选择可用模板,选择“ProcessingWF_QE
active\PWF_QE_Reporter_Based_Quan_Seque tHT_Percolator.pdProcessingWF”。
4. 若要进行 Consensus Workflow,选择“ConsensusWF CWF_Comprehensive_Enhanced_Annotation_Quan pdConsensusWF”。
5. 选定第一部分中创建的 Quantification Method,然后选定 Control channel Selection。
6. 导入要处理的 .raw 文件。图 2 示例中导入了采用两个不同隔离窗口设置的四份平行分析产生的原始数据文件。
7. 选择 OK,数据文件会在新窗口打开。
8.
对于涉及平行分析的复杂研究,推荐使用 Study Factors 管理功能进行结果分组、归一化以及展示。若要添加 Study
Factors,在当前研究页面选择 Study Definition tab,选择 Add
来添加类别或数字类型的因素。键入因素名称和所有相关因素(图 3)。如无需使用 Study Factor,直接进入第四部分的工作流程设置操作。
9. 在 Input Files tab 条目下应该能够显示导入的原始文件。可以用左侧三角形图标展开查看文件细节。根据实验设置为每个文件和报告离子指明 Sample Type 和 Study Factors。
10. 完成后查阅 Sample tab——此时所有研究因素应当已经自动更新。
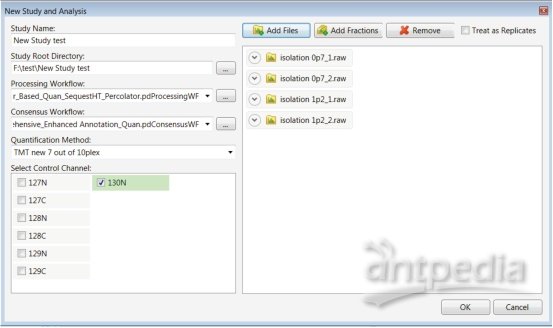
图 2. 全新的研究和分析设置对话界面。
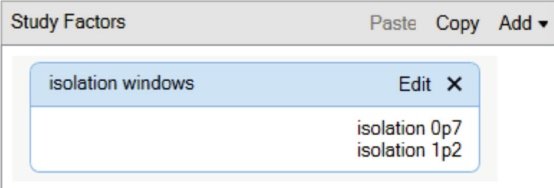
图 3. 在 Study Factor 管理界面中添加新的研究因素。
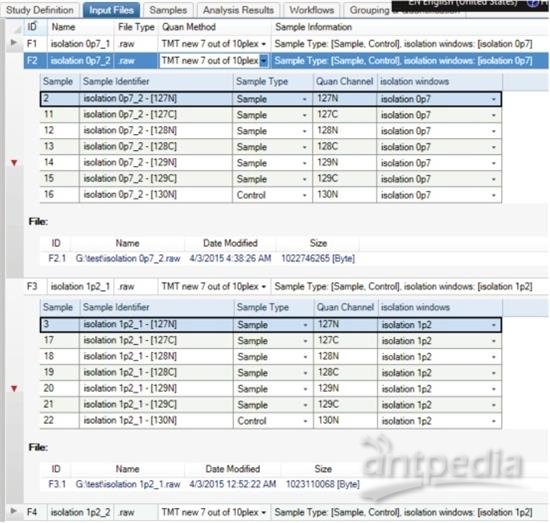
图 4. 单个样品定量设置的 Study Factors 和定量分析通道
