蛋白质互作网络(Protein-Protein Interaction Networks,PPI)是由蛋白通过彼此之间的相互作用构成,来参与生物信号传递、基因表达调节、能量和物质代谢及细胞周期调控等生命过程的各个环节。
String数据库(https://string-db.org/)是一个搜索已知蛋白质之间和预测蛋白质之间相互作用的数据库,该数据库可应用于五千多个物种,包含两千四百万种蛋白的,大于2000万种蛋白质之间的相互作用连接。
目前一般都采用String数据库来研究蛋白互作网络,那么下面来介绍一下这个数据库的基本使用方法。
1
查询与某一个蛋白间有互作关系的蛋白有哪些?
(1)首先,打开String网站,点击左侧的protein by name,然后在右侧输入蛋白ID(可以是uniprot蛋白ID也可以是基因名)和物种名,点击search即可;
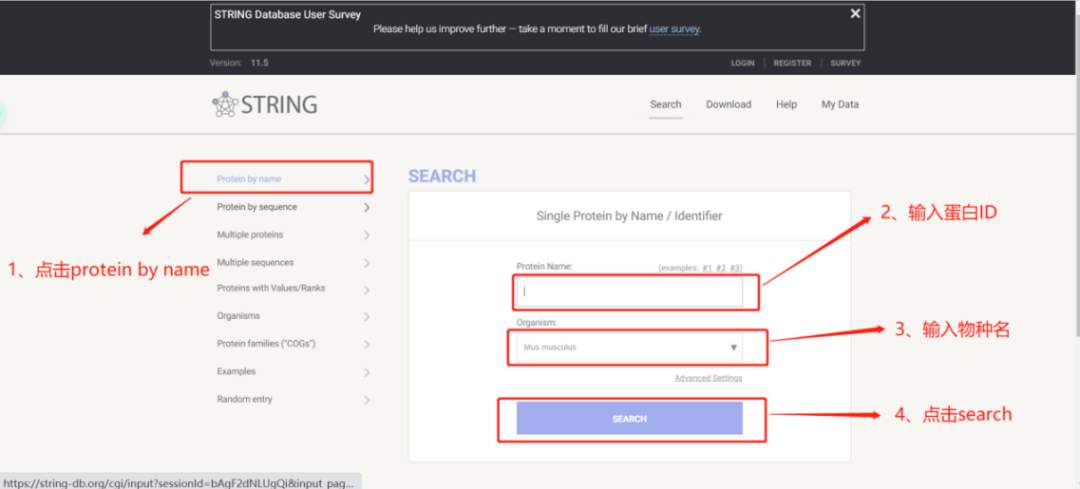
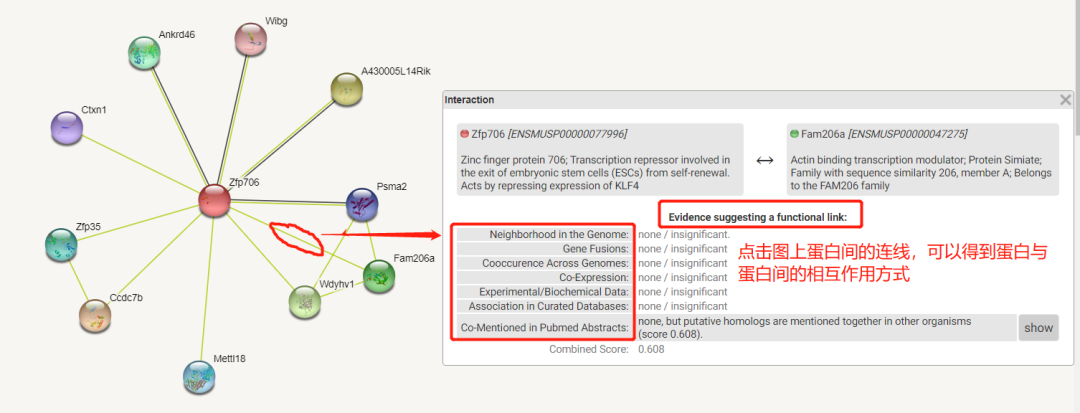
(2)然后(例如输入小鼠蛋白Znf706),则可得到与该蛋白有互作关系的相关蛋白信息,点击legend可得到目的蛋白与互作蛋白间的连接度信息;


(3)点击PPI图上的彩色圆球可以得到蛋白的结构信息,点击蛋白与蛋白间的连线可以得到蛋白间相互作用的类型(不同颜色代表不同的作用类型,数据库将作用类型分为7大类,分别是基因邻接、基因融合、基因共表达、实验数据、文本挖掘数据、数据库数据、在PubMed Abstracts中共同提及)。

2
绘制蛋白与蛋白间PPI图。
(1)首先,打开String网站,点击左侧的multiple proteins,然后在右侧输入蛋白ID(可以是uniprot蛋白ID也可以是基因名)和物种名,点击search即可;
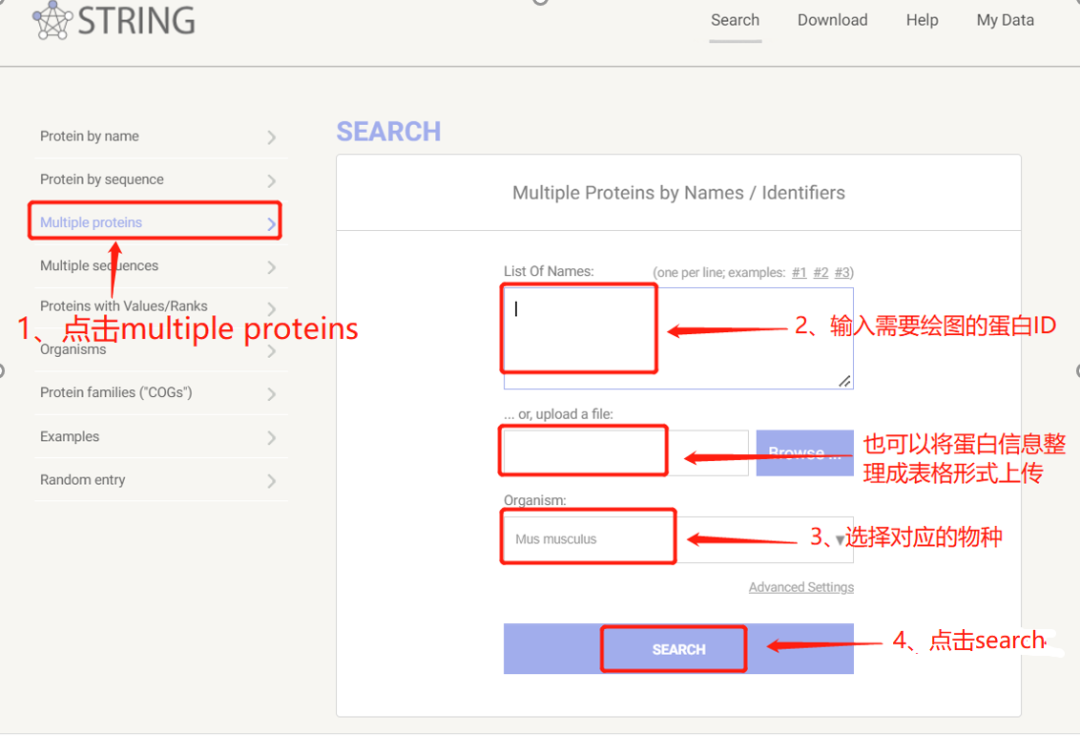
(2)点击search即可得到蛋白-蛋白相互作用结果。有老师会发现我们项目报告里面提供的结果和String网站做出来的PPI图有一些不太一样,主要是因为与网站的默认阈值设置的不同,这个时候只需要将minimum required interaction score设置成low confidence即可;

点击exports即可查看蛋白与蛋白间的连接度;

3
使用Cytoscape软件对PPI图进行美化。
目前String上的图可能不够满足发文个性化要求,因此会需要用Cytoscape软件进行图片美化,关于Cytoscape图片绘制方法,我们有绘制相关教程,需要的话,私信小鹿哦。

(点击图片可以了解Cytoscape)
.
文末看点|lumingbio
上海鹿明生物科技有限公司多年来,一直专注于生命科学和生命技术领域,是国内早期开展以蛋白组学和代谢组学为基础的多层组学整合实验与分析的团队。目前在多层组学研究已经有了成熟的技术方法,欢迎各位老师前来咨询哦~

同时,鹿明生物B站上线了5大频道板块,分别在空间代谢组学、生信分析、多层组学、代谢组学方向为各位科研老师提供有效的方法工具和思路~其中,生信板块也拥有着观看量1.5万的生信爆款视频~欢迎各位老师访问,鹿明生物B站:
https://space.bilibili.com/388691543

长按扫码咨询鹿明生物技术工程师
猜你还想看
1、用一个蛋白叩开uniprot的大门——uniprot入门手册
2、蛋白研究常用数据库 | UniProt数据库介绍及使用说明
END
叮当|撰文
欢迎转发到朋友圈
本文系鹿明生物原创
转载请注明本文转自鹿明生物

我知道你在看哟


点击“阅读原文”了解更多