2.3数据处理
采用Thermo ScientificTM Protein Deconvolution 3.0对原始质谱图进行去卷积。
参数如下:
Noise compensation | ON |
Minimum adjacent charges | 1 to 3 |
Noise Rejection | 95% confidence |
3实验结果
本实验通过直接进样方式,分别设置Orbitrap分辨率为17500,35000,70000, ADCs药物的原始质谱图如图3,ADCs药物的质谱峰主要分布在m/z 5000-7000范围内,具有理想的信噪比。选取两组质谱峰进行放大(图4所示)可以发现,当逐渐提高质谱分辨率时,主峰逐渐与加合离子峰分离。分辨率越高,分离效果越明显。
经Protein Deconvolution 3.0软件去卷积处理之后的不同分辨率下的ADCs药物分子质量分布如图5所示,根据ADCs药物单抗的氨基酸序列和小分子药物的理论分子量进行计算,将观察到的质谱峰进行归属,从图中我们观察到,五个主峰呈现等质量间隔(约2635Da),由此可推断该单抗分子结合了不同数目的药物小分子。结合cysteine-linked ADCs的特点,判断主峰依次为结合了0、2、4、6、8个小分子药物的ADCs混合物,该结果与理论预期一致。

图3 不同分辨率设置下(17500,35000,70000)ADCs药物的原始质谱图

图4 不同分辨率设置下(17500,35000,70000)ADCs药物局部放大质谱图

图5 不同分辨率设置下(17500,35000,70000)ADCs药物去卷积后结果
Resolution | Drug Load | Measured MW (Da) | Theoretical MW (Da) | Delta M (Da) |
17500 | D0 | 145111 | 145103 | 7.7 |
D2 | 147739 | 147738 | 0.3 | |
D4 | 150378 | 150374 | 4.1 | |
D6 | 153016 | 153009 | 6.6 | |
D8 | 155649 | 155644 | 4.4 | |
35000 | D0 | 145103 | 145103 | 0.3 |
D2 | 147740 | 147738 | 1.6 | |
D4 | 150375 | 150374 | 1.1 | |
D6 | 153010 | 153009 | 1.4 | |
D8 | 155646 | 155644 | 1.6 | |
70000 | D0 | 145104 | 145103 | 0.6 |
D2 | 147741 | 147738 | 2.7 | |
D4 | 150376 | 150374 | 1.9 | |
D6 | 153011 | 153009 | 2.4 | |
D8 | 155644 | 155644 | 0.2 |
表1不同分辨率(17500,35000,70000)下去卷积后的精确分子量和质量偏差
不同分辨率(17500,35000,70000)下去卷积后的精确分子量如表1所示,比较发现,当分辨率设置为17500时,由于无法实现主峰和加合离子峰的有效分离,质量与理论值偏差较大,最大偏差达到7.7Da。当分辨率逐渐提升到35000,主峰逐渐与加合离子峰分离,质量偏差控制在0.3-1.6Da,具有极佳的质量准确度。当分辨率逐渐进一步提升到70000时,主峰与加合离子峰分离度进一步提高,同样可获得理想的质量准确度(0.2-2.7Da),满足测定需求。
根据质谱峰的峰强度信息,可计算该药物的DAR值,该数值对于ADCs药物的有效性评估至关重要。以分辨率设置35000下质谱图去卷积结果为例(如图6所示),按照DAR = Σ(relative peak area×number of loaded drugs)/100计算DAR值,获知该ADCs药物DAR=3.9。
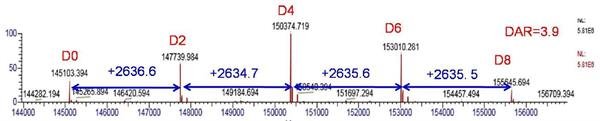
图6 分辨率设置35000下质谱图去卷积后ADCs药物质量分布图(D0-D8表示载有不同药物分子数的ADCs混合物)
4结论
本文采用Exactive Plus EMR质谱仪,直接进样方式,突破了传统的RPLC/MS平台无法进行cysteine-linked ADCs分析的瓶颈,建立了cysteine-linked ADCs的精确分子量测定方法,为cysteine-linked ADCs 单抗药物研发和生产检测提供了高效、快速的分析平台。实验结果表明Exactive Plus EMR质谱仪凭借其超高的分辨率、超快的扫描速度、超高的质量精度、超高的灵敏度以及拓展的质量范围,极大地完善和推动了ADCs药物的鉴定分析。
参考文献
1. Albert J R Heck et al. Nat. Methods 2008, 5(4), 927-933.
2. Sara Rosati et al. Nature Protocols 2014,9(4) , 967-976