4.转录组、蛋白组揭示miR-137调控底物。
蛋白组结果发现:Mir137–/–组versus Mir137+/+组, Mir137+/–组versus Mir137+/+组, and Mir137–/–组versus Mir137+/–组,分别筛选到417、94和76个差异表达蛋白。这些蛋白与DNA replication, nervous system development, and chromatinremodeling,peptidase activity regulation, acute-phaseresponse, and regulation of neurotransmitter secretion等生物过程有关。其中有41个上调蛋白和9个下调蛋白,被预测为miR-137的底物。通过与RNAseq结果的进一步比对,41个上调蛋白中有37个蛋白对应的基因,在mRNA表达水平没有显著表达差异,表明上述基因可能是miR-137通过转录后调控模式所直接调控得底物。
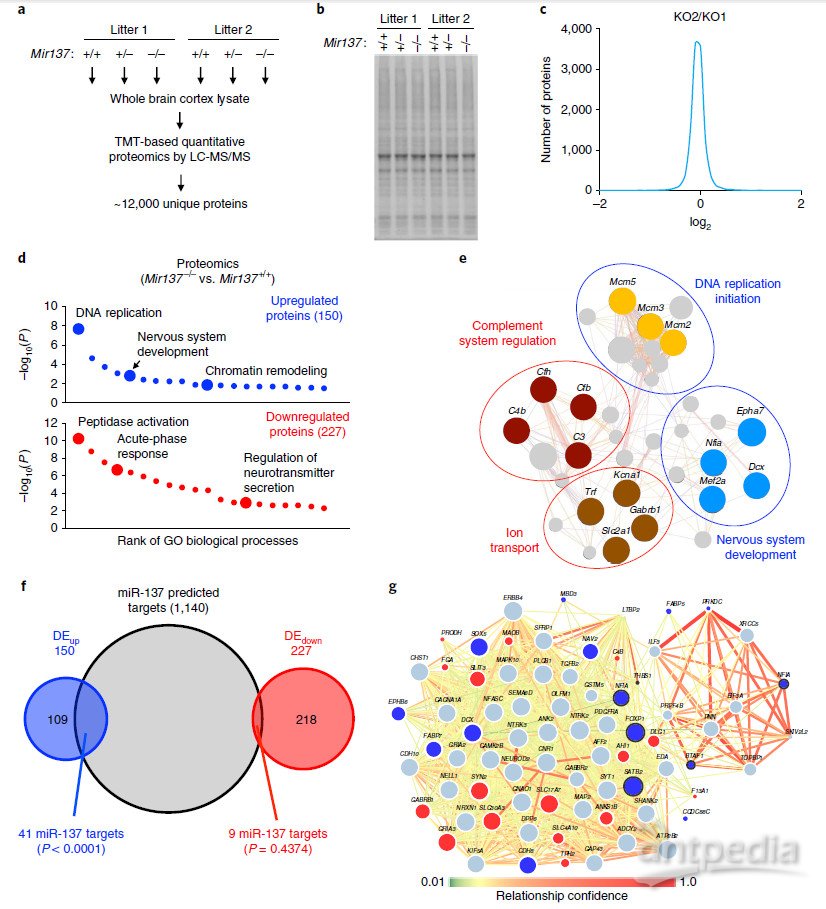
Fig. 5 | Systematic identification of in vivo mRNA targetsof miR-137 by integrating proteomic, transcriptomic, and bioinformaticanalyses.
5.确证Pde10a基因是miR-137的直接调控底物
在上述37个基因中,作者挑选了5个表达上调最显著的蛋白对应的基因,以及5个神经功能相关基因。采用luciferase reporter assay +UTR突变的方法,证实Pde10a基因是miR-137的直接调控底物

Fig. 6 | Pde10a is akey mRNA target of miR-137.
6.后续研究
抑制Pde10a的表达能够减缓miR-137 KO引起的神经功能失调。Pde10a KO可逆转了miR-137 KO引起的神经功能失调。
总结与扩展
该文章思路清晰:围绕前期基因研究中发现的可能具有重要作用的miRNA展开。基于KO动物模型,首先评价了miRNA的生物功能。然后利用多组学的数据,筛选可能的miRNA底物,再利用经典方法进行直接底物验证;最后再评价底物被干预后的表型变化。从而实现对目标miRNA功能和作用机制的解析。
其中miRNA底物筛选的方法,值得借鉴。因为,常规通过序列比对预测出的底物,还是存在很多的不准确性。而蛋白质组的分析可以明确告诉我们,到底哪些蛋白产物确实发生了相应的表达变化,蛋白产物的表达水平是miRNA底物判定的最重要依据。同时,如果差异表达蛋白所对应的mRNA并没有相应改变,则可进一步确定该基因的调控方式并不是因为基因转录水平的变化,而是miRNA参与的转录后水平的调控(另外还有一种途径是miRNA的结合,引起了mRNA的降解)。所以,在底物预测的基础上,蛋白组+转录组可以更加准确、有效地筛选miRNA的底物,并提供更全面、更系统的信息。

