宏基因组测序,是一种直接对某一特定环境中微生物基因组进行分析,通过构建宏基因组文库,利用基因组学的研究策略研究微生物群体基因组成及功能,解读微生物群体的多样性与丰度,是研究微生物功能多样性、开发新的生理活性物质等的一种新理念和新方法。对于研究微生物与环境的关系、环境治理和微生物资源的利用有着重要的理论和现实意义。
产品优势:
专业的研究方案:对测序结果组装分析后,得到微生物群体基因组及功能、分析微生物群体中物种和基因的多样性和丰度,微生物菌落结构与宿主(或环境)之间的相互关系等
更合理的研究方法:在分析过程中,采用一些更为准确的方法,从而得到更为可靠的分析结果
新的分析方法:增加了MGS等宏基因组分析的方法,对样品中的信息得到更大的解析
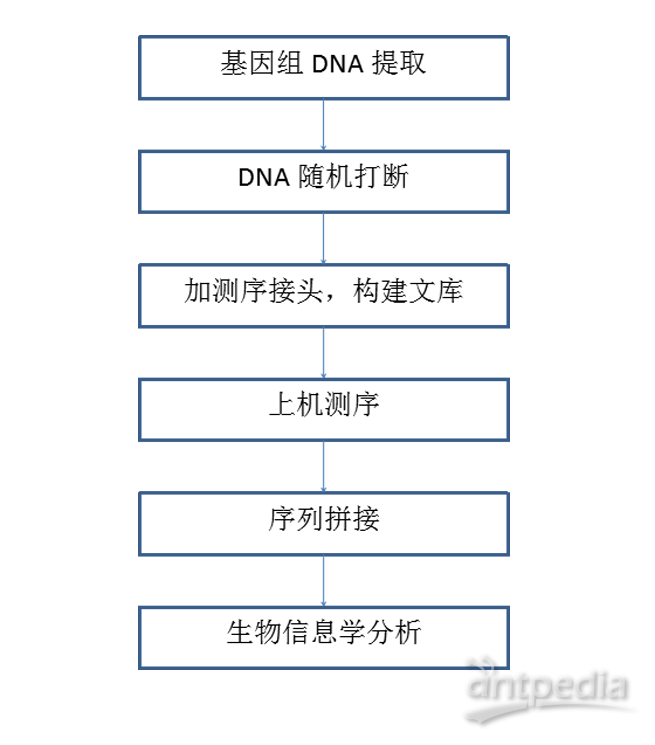
技术路线:
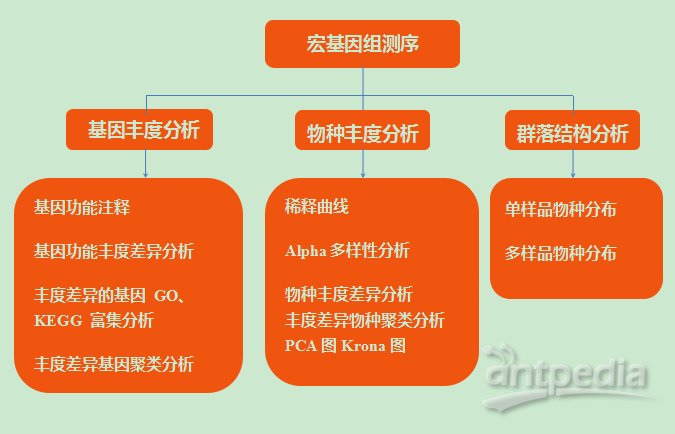
分析内容:
样品要求:
1.样品类型:环境样品 DNA;
2.样品浓度:≥50 ng/ul;
3.样品总量:≥15ug;单次文库制备用量为5ug,为保证实验的顺利进行,因此需保证样品总量大于3次以上的建库用量;
4.样品纯度:OD260/280为1.8~2.2;
5.电泳要求:主带清晰,无降解或轻度降解。
案例分析:
1、宏基因组揭示人体肠道微生物多样性
本研究利用宏基因组,对27位健康哈扎人和11位意大利人进行肠道微生物分析。结果表明,哈扎人肠道微生物中与氨基酸代谢和多糖代谢相关基因丰度较高,意大利人肠道微生物中与单糖(葡萄糖、蔗糖、果糖等)代谢、氨基酸代谢有关基因丰度较高;两者之间的差异可能与其饮食有关。此外,哈扎人肠道微生物中抗生素耐药性基因组成与土壤、水体来源的抗生素耐药性组成相似,而意大利人的抗生素耐药性则跟其生活环境和抗生素使用范围类似。人体肠道微生物的研究有助于了解其在人体生理机能方面的作用,同时阐明了人类生活和生存方式的多样性。
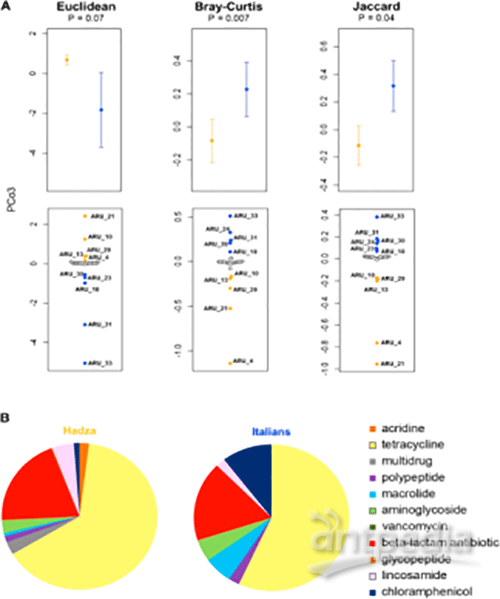
肠道微生物抗生素耐药性分析
2、宏基因组学研究揭示肠道菌群之间的生命运动规律
本研究收集了181个来自于中国人肠道菌群的样本,其中98个中国肝硬化患者的粪便样品及83个健康中国人志愿者的粪便样品,验证阶段收集31个健康人及25个肝硬化患者的MGS丰度。从中获得269万个非冗余的人体肠道微生物菌群的基因集,建立了肝病肠道菌群基因集,其中36.1%的基因是发现的。共有75,245个基因在肝硬化患者和健康人志愿者中呈现显着差异,可以归类到66个基因簇,该基因簇为肝硬化的生物标记物,其中在肝硬化患者中富集的是28个基因簇,健康志愿者中富集的是38个基因簇。通过对粪便微生物中15个基因的检测可以诊断肝硬化,同时找到的细菌标志物为肝硬化微生态制剂的研发也提供了方向。

病人(n=123)和健康人(n=114)个体肠道菌群中富集的不同丰度的MGS
参考文献:
1. Metagenome Sequencing of the Hadza Hunter-Gatherer Gut Microbiota (Cell Press, 2015, IF = 9.571)
2. Alterations of the human gut microbiome in liver cirrhosis. ( Nature, 2014, IF = 41.456)